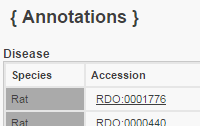
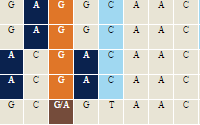
(+)-schisandrin B multiple interactions ISO Spsb4 (Rattus norvegicus) 6480464 schizandrin B inhibits the reaction [Carbon Tetrachloride results in decreased expression of SPSB4 mRNA] CTD PMID:31150632 1,2-dichloroethane affects expression ISO Spsb4 (Mus musculus) 6480464 ethylene dichloride affects the expression of SPSB4 mRNA CTD PMID:28960355 1-naphthyl isothiocyanate increases expression ISO Spsb4 (Rattus norvegicus) 6480464 1-Naphthylisothiocyanate results in increased expression of SPSB4 mRNA CTD PMID:25380136 and PMID:30723492 17beta-estradiol decreases expression ISO Spsb4 (Rattus norvegicus) 6480464 Estradiol results in decreased expression of SPSB4 mRNA CTD PMID:35192832 2,2',4,4'-Tetrabromodiphenyl ether decreases expression ISO Spsb4 (Rattus norvegicus) 6480464 2 more ... CTD PMID:27291303 2,3,7,8-tetrachlorodibenzodioxine affects expression ISO Spsb4 (Mus musculus) 6480464 Tetrachlorodibenzodioxin affects the expression of SPSB4 mRNA CTD PMID:21570461 2,3,7,8-tetrachlorodibenzodioxine decreases expression ISO Spsb4 (Rattus norvegicus) 6480464 Tetrachlorodibenzodioxin results in decreased expression of SPSB4 mRNA CTD PMID:33387578 2,3,7,8-tetrachlorodibenzodioxine affects expression ISO Spsb4 (Rattus norvegicus) 6480464 Tetrachlorodibenzodioxin affects the expression of SPSB4 mRNA CTD PMID:32109520 4,4'-diaminodiphenylmethane increases expression ISO Spsb4 (Rattus norvegicus) 6480464 4 and 4'-diaminodiphenylmethane results in increased expression of SPSB4 mRNA CTD PMID:25380136 4-hydroxyphenyl retinamide increases expression ISO Spsb4 (Mus musculus) 6480464 Fenretinide results in increased expression of SPSB4 mRNA CTD PMID:28973697 4-hydroxyphenyl retinamide decreases expression ISO Spsb4 (Mus musculus) 6480464 Fenretinide results in decreased expression of SPSB4 mRNA CTD PMID:28973697 6-propyl-2-thiouracil increases expression ISO Spsb4 (Rattus norvegicus) 6480464 Propylthiouracil results in increased expression of SPSB4 mRNA CTD PMID:24780913 and PMID:30047161 acetamide increases expression ISO Spsb4 (Rattus norvegicus) 6480464 acetamide results in increased expression of SPSB4 mRNA CTD PMID:31881176 acrylamide decreases expression ISO Spsb4 (Rattus norvegicus) 6480464 Acrylamide results in decreased expression of SPSB4 mRNA CTD PMID:28959563 acrylamide decreases expression EXP 6480464 Acrylamide results in decreased expression of SPSB4 mRNA CTD PMID:32763439 all-trans-retinoic acid increases expression ISO Spsb4 (Rattus norvegicus) 6480464 Tretinoin results in increased expression of SPSB4 mRNA CTD PMID:20488242 amitrole increases expression ISO Spsb4 (Rattus norvegicus) 6480464 Amitrole results in increased expression of SPSB4 mRNA CTD PMID:30047161 antirheumatic drug increases expression EXP 6480464 Antirheumatic Agents results in increased expression of SPSB4 mRNA CTD PMID:24449571 arsane affects methylation EXP 6480464 Arsenic affects the methylation of SPSB4 gene CTD PMID:25304211 arsenic atom affects methylation EXP 6480464 Arsenic affects the methylation of SPSB4 gene CTD PMID:25304211 arsenite(3-) increases methylation EXP 6480464 arsenite results in increased methylation of SPSB4 promoter CTD PMID:23974009 benzo[a]pyrene decreases expression ISO Spsb4 (Mus musculus) 6480464 Benzo(a)pyrene results in decreased expression of SPSB4 mRNA CTD PMID:19770486 and PMID:27195522 benzo[a]pyrene affects methylation EXP 6480464 Benzo(a)pyrene affects the methylation of SPSB4 promoter CTD PMID:27901495 benzo[a]pyrene decreases methylation EXP 6480464 Benzo(a)pyrene results in decreased methylation of SPSB4 3' UTR CTD PMID:27901495 benzo[a]pyrene increases methylation EXP 6480464 Benzo(a)pyrene results in increased methylation of SPSB4 5' UTR CTD PMID:27901495 bisphenol A affects expression ISO Spsb4 (Rattus norvegicus) 6480464 bisphenol A affects the expression of SPSB4 mRNA CTD PMID:25181051 and PMID:30903817 bisphenol A decreases expression ISO Spsb4 (Rattus norvegicus) 6480464 bisphenol A results in decreased expression of SPSB4 mRNA CTD PMID:34947998 bisphenol A increases expression ISO Spsb4 (Rattus norvegicus) 6480464 bisphenol A results in increased expression of SPSB4 mRNA CTD PMID:32145629 bisphenol A increases methylation ISO Spsb4 (Rattus norvegicus) 6480464 bisphenol A results in increased methylation of SPSB4 gene CTD PMID:28505145 bromobenzene increases expression ISO Spsb4 (Rattus norvegicus) 6480464 bromobenzene results in increased expression of SPSB4 mRNA CTD PMID:32479839 buta-1,3-diene decreases expression ISO Spsb4 (Mus musculus) 6480464 1 and 3-butadiene results in decreased expression of SPSB4 mRNA CTD PMID:29038090 carbon nanotube decreases expression ISO Spsb4 (Mus musculus) 6480464 Nanotubes more ... CTD PMID:25620056 carbon nanotube increases expression ISO Spsb4 (Mus musculus) 6480464 Nanotubes and Carbon analog results in increased expression of SPSB4 mRNA CTD PMID:25554681 CGP 52608 multiple interactions EXP 6480464 CGP 52608 promotes the reaction [RORA protein binds to SPSB4 gene] CTD PMID:28238834 choline multiple interactions ISO Spsb4 (Mus musculus) 6480464 [Methionine deficiency co-treated with Choline deficiency co-treated with Folic Acid deficiency] results in increased methylation of SPSB4 gene CTD PMID:20938992 ciguatoxin CTX1B affects expression ISO Spsb4 (Mus musculus) 6480464 Ciguatoxins affects the expression of SPSB4 mRNA CTD PMID:18353800 decabromodiphenyl ether decreases expression ISO Spsb4 (Rattus norvegicus) 6480464 decabromobiphenyl ether results in decreased expression of SPSB4 mRNA CTD PMID:23640034 decabromodiphenyl ether increases expression ISO Spsb4 (Rattus norvegicus) 6480464 decabromobiphenyl ether results in increased expression of SPSB4 mRNA CTD PMID:23640034 dibutyl phthalate increases expression ISO Spsb4 (Mus musculus) 6480464 Dibutyl Phthalate results in increased expression of SPSB4 mRNA CTD PMID:17361019 and PMID:21266533 dichloroacetic acid increases expression ISO Spsb4 (Mus musculus) 6480464 Dichloroacetic Acid results in increased expression of SPSB4 mRNA CTD PMID:28962523 dorsomorphin multiple interactions EXP 6480464 [NOG protein co-treated with mercuric bromide co-treated with dorsomorphin co-treated with 4-(5-benzo(1 more ... CTD PMID:27188386 doxorubicin decreases expression EXP 6480464 Doxorubicin results in decreased expression of SPSB4 mRNA CTD PMID:29803840 folic acid multiple interactions ISO Spsb4 (Mus musculus) 6480464 [Methionine deficiency co-treated with Choline deficiency co-treated with Folic Acid deficiency] results in increased methylation of SPSB4 gene CTD PMID:20938992 folic acid increases expression ISO Spsb4 (Mus musculus) 6480464 Folic Acid results in increased expression of SPSB4 mRNA CTD PMID:25629700 furan increases expression ISO Spsb4 (Rattus norvegicus) 6480464 furan results in increased expression of SPSB4 mRNA CTD PMID:25539665 gentamycin decreases expression ISO Spsb4 (Rattus norvegicus) 6480464 Gentamicins results in decreased expression of SPSB4 mRNA CTD PMID:33387578 glafenine increases expression ISO Spsb4 (Rattus norvegicus) 6480464 Glafenine results in increased expression of SPSB4 mRNA CTD PMID:24136188 L-methionine multiple interactions ISO Spsb4 (Mus musculus) 6480464 [Methionine deficiency co-treated with Choline deficiency co-treated with Folic Acid deficiency] results in increased methylation of SPSB4 gene CTD PMID:20938992 lipopolysaccharide increases expression EXP 6480464 Lipopolysaccharides results in increased expression of SPSB4 mRNA CTD PMID:35811015 lipopolysaccharide multiple interactions EXP 6480464 [S-(1 and 2-dichlorovinyl)cysteine affects the susceptibility to Lipopolysaccharides] which results in increased expression of SPSB4 mRNA CTD PMID:35811015 mercury dibromide increases expression EXP 6480464 mercuric bromide results in increased expression of SPSB4 mRNA CTD PMID:26272509 mercury dibromide multiple interactions EXP 6480464 [NOG protein co-treated with mercuric bromide co-treated with dorsomorphin co-treated with 4-(5-benzo(1 and 3)dioxol-5-yl-4-pyridin-2-yl-1H-imidazol-2-yl)benzamide] results in increased expression of SPSB4 mRNA CTD PMID:27188386 methimazole increases expression ISO Spsb4 (Rattus norvegicus) 6480464 Methimazole results in increased expression of SPSB4 mRNA CTD PMID:30047161 methoxychlor affects methylation ISO Spsb4 (Rattus norvegicus) 6480464 Methoxychlor affects the methylation of SPSB4 gene CTD PMID:35440735 N-benzyloxycarbonyl-L-leucyl-L-leucyl-L-leucinal decreases expression ISO Spsb4 (Mus musculus) 6480464 benzyloxycarbonylleucyl-leucyl-leucine aldehyde results in decreased expression of SPSB4 mRNA CTD PMID:25566086 N-benzyloxycarbonyl-L-leucyl-L-leucyl-L-leucinal multiple interactions ISO Spsb4 (Mus musculus) 6480464 MYBPC3 protein affects the reaction [benzyloxycarbonylleucyl-leucyl-leucine aldehyde results in decreased expression of SPSB4 mRNA] CTD PMID:25566086 N-nitrosodimethylamine increases expression ISO Spsb4 (Rattus norvegicus) 6480464 Dimethylnitrosamine results in increased expression of SPSB4 mRNA CTD PMID:25380136 panobinostat multiple interactions EXP 6480464 [NOG protein co-treated with Panobinostat co-treated with dorsomorphin co-treated with 4-(5-benzo(1 and 3)dioxol-5-yl-4-pyridin-2-yl-1H-imidazol-2-yl)benzamide] results in increased expression of SPSB4 mRNA CTD PMID:27188386 panobinostat increases expression EXP 6480464 panobinostat results in increased expression of SPSB4 mRNA CTD PMID:26272509 paracetamol increases expression ISO Spsb4 (Rattus norvegicus) 6480464 Acetaminophen results in increased expression of SPSB4 mRNA CTD PMID:32479839 and PMID:33387578 phenylmercury acetate increases expression EXP 6480464 Phenylmercuric Acetate results in increased expression of SPSB4 mRNA CTD PMID:26272509 phenylmercury acetate multiple interactions EXP 6480464 [NOG protein co-treated with Phenylmercuric Acetate co-treated with dorsomorphin co-treated with 4-(5-benzo(1 and 3)dioxol-5-yl-4-pyridin-2-yl-1H-imidazol-2-yl)benzamide] results in increased expression of SPSB4 mRNA CTD PMID:27188386 pirinixic acid increases expression ISO Spsb4 (Mus musculus) 6480464 pirinixic acid results in increased expression of SPSB4 mRNA CTD PMID:18301758 pirinixic acid decreases expression ISO Spsb4 (Mus musculus) 6480464 pirinixic acid results in decreased expression of SPSB4 mRNA CTD PMID:20813756 more ... pirinixic acid multiple interactions ISO Spsb4 (Mus musculus) 6480464 PPARA protein affects the reaction [pirinixic acid results in decreased expression of SPSB4 mRNA] CTD PMID:21318169 potassium dichromate decreases expression ISO Spsb4 (Mus musculus) 6480464 Potassium Dichromate results in decreased expression of SPSB4 mRNA CTD PMID:23608068 resveratrol multiple interactions ISO Spsb4 (Rattus norvegicus) 6480464 [resveratrol co-treated with Streptozocin] results in increased expression of SPSB4 mRNA CTD PMID:25905778 resveratrol multiple interactions EXP 6480464 [Plant Extracts co-treated with Resveratrol] results in decreased expression of SPSB4 mRNA CTD PMID:23557933 S-(1,2-dichlorovinyl)-L-cysteine multiple interactions EXP 6480464 [S-(1 and 2-dichlorovinyl)cysteine affects the susceptibility to Lipopolysaccharides] which results in increased expression of SPSB4 mRNA CTD PMID:35811015 SB 431542 multiple interactions EXP 6480464 [NOG protein co-treated with mercuric bromide co-treated with dorsomorphin co-treated with 4-(5-benzo(1 more ... CTD PMID:27188386 silicon dioxide decreases expression ISO Spsb4 (Mus musculus) 6480464 Silicon Dioxide results in decreased expression of SPSB4 mRNA CTD PMID:23221170 sodium arsenite decreases expression ISO Spsb4 (Mus musculus) 6480464 sodium arsenite results in decreased expression of SPSB4 mRNA CTD PMID:37682722 streptozocin multiple interactions ISO Spsb4 (Rattus norvegicus) 6480464 [resveratrol co-treated with Streptozocin] results in increased expression of SPSB4 mRNA CTD PMID:25905778 sulfadimethoxine increases expression ISO Spsb4 (Rattus norvegicus) 6480464 Sulfadimethoxine results in increased expression of SPSB4 mRNA CTD PMID:30047161 sunitinib decreases expression EXP 6480464 Sunitinib results in decreased expression of SPSB4 mRNA CTD PMID:31533062 tamoxifen affects expression ISO Spsb4 (Mus musculus) 6480464 Tamoxifen affects the expression of SPSB4 mRNA CTD PMID:20937368 testosterone increases expression ISO Spsb4 (Mus musculus) 6480464 Testosterone results in increased expression of SPSB4 mRNA CTD PMID:21669218 tetrachloromethane affects expression ISO Spsb4 (Mus musculus) 6480464 Carbon Tetrachloride affects the expression of SPSB4 mRNA CTD PMID:17484886 tetrachloromethane decreases expression ISO Spsb4 (Rattus norvegicus) 6480464 Carbon Tetrachloride results in decreased expression of SPSB4 mRNA CTD PMID:31150632 tetrachloromethane multiple interactions ISO Spsb4 (Rattus norvegicus) 6480464 schizandrin B inhibits the reaction [Carbon Tetrachloride results in decreased expression of SPSB4 mRNA] CTD PMID:31150632 tetrachloromethane decreases expression ISO Spsb4 (Mus musculus) 6480464 Carbon Tetrachloride results in decreased expression of SPSB4 mRNA CTD PMID:27339419 and PMID:31919559 thioacetamide increases expression ISO Spsb4 (Rattus norvegicus) 6480464 Thioacetamide results in increased expression of SPSB4 mRNA CTD PMID:23411599 trichloroethene increases methylation ISO Spsb4 (Rattus norvegicus) 6480464 Trichloroethylene results in increased methylation of SPSB4 gene CTD PMID:27618143 trichloroethene decreases expression ISO Spsb4 (Rattus norvegicus) 6480464 Trichloroethylene results in decreased expression of SPSB4 mRNA CTD PMID:33387578 trichostatin A increases expression EXP 6480464 trichostatin A results in increased expression of SPSB4 mRNA CTD PMID:26272509 trichostatin A multiple interactions EXP 6480464 [NOG protein co-treated with trichostatin A co-treated with dorsomorphin co-treated with 4-(5-benzo(1 and 3)dioxol-5-yl-4-pyridin-2-yl-1H-imidazol-2-yl)benzamide] results in increased expression of SPSB4 mRNA CTD PMID:27188386 valproic acid increases expression ISO Spsb4 (Mus musculus) 6480464 Valproic Acid results in increased expression of SPSB4 mRNA CTD PMID:21427059 valproic acid multiple interactions EXP 6480464 [NOG protein co-treated with Valproic Acid co-treated with dorsomorphin co-treated with 4-(5-benzo(1 and 3)dioxol-5-yl-4-pyridin-2-yl-1H-imidazol-2-yl)benzamide] results in increased expression of SPSB4 mRNA CTD PMID:27188386 valproic acid increases expression EXP 6480464 Valproic Acid results in increased expression of SPSB4 mRNA CTD PMID:23179753 more ... valproic acid decreases methylation EXP 6480464 Valproic Acid results in decreased methylation of SPSB4 gene CTD PMID:29154799 vancomycin increases expression ISO Spsb4 (Mus musculus) 6480464 Vancomycin results in increased expression of SPSB4 mRNA CTD PMID:18930951