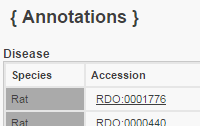
Imported Disease Annotations - CTDTerm | Qualifier | Evidence | With | Reference | Notes | Source | Original Reference(s) | Experimental Liver Cirrhosis | | EXP | | 11554173 | CTD Direct Evidence: marker/mechanism | CTD | PMID:25380136 | | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|
|
Gene-Chemical Interaction Annotations Click to see Annotation Detail View
Gene Ontology Annotations Click to see Annotation Detail View
Biological Process
Cellular Component
Molecular Function